从全基因组关联研究(GWAS)中估计基于单核苷酸多态性(SNP)的遗传力和遗传相关性的方法,已成为研究人类复杂性状遗传学和常见疾病遗传结构,以及揭示疾病之间关联的基本统计工具。
通常,对人类复杂性状的遗传相关性假设交配是随机的(随机交配),即在一个有性繁殖的生物群体中,一个雌性(或雄性)个体与任一一个相反性别的个体交配的概率相等。也就是说,任何一对雌雄结合都是随机的,不受选型交配的影响。
然而,在现实世界中,人们往往会因为共同的兴趣爱好和社会结构而结成伴侣。因此,在之前的研究中,一些被归因于共享基因的遗传相关性可能代表了错误的统计假设。
近日,加州大学洛杉矶分校的研究人员在国际顶尖学术期刊 Science 上发表了题:Cross-trait assortative mating is widespread and inflates genetic correlation estimates 的研究论文。
这项研究显示,遗传相关性评估的实质性变化可以通过交叉表型相关性来解释。目前评估性状之间遗传联系的方法未能考虑到交配模式。因此,许多关于性状和疾病共享遗传信号强度的研究结果可能被夸大了。

近年来,通过使用基因组测序技术,科学家们试图了解性状与疾病风险之间的遗传联系,并希望共享遗传学发现以为解决疾病提供线索。然而,这些分析结果值得警惕,因为许多表型相似程度有限的性状,也会显示出一定的遗传相关性。例如,对体重指数(BMI)和受教育程度之间的基因重叠估计很可能反映了由“交叉性状选型交配”引起的种群结构,即配偶在不同性状之间表现出交叉相关性的现象。因此,研究团队对过度依赖遗传相关性评估提出了警告:这种估计受到了非生物因素的干扰,并且比以前认识到的要严重得多。
在这项新研究中,研究团队引入了被忽视的潜在偏见来源:交叉性状选型交配(xAM),他们首先使用了来自英国和丹麦超过15万参与者的两个大型人口样本系统评估了 xAM 对遗传相关性估计的影响,并在先前广泛的研究表型中编制大量交叉相关性图集。研究人员观察到,xAM 会影响许多表型,并且表型交叉相关性估计与遗传相关性估计密切相关。这些表型交叉相关性可以解释相同性状对基于经验标记的预期遗传相关性的很大一部分。
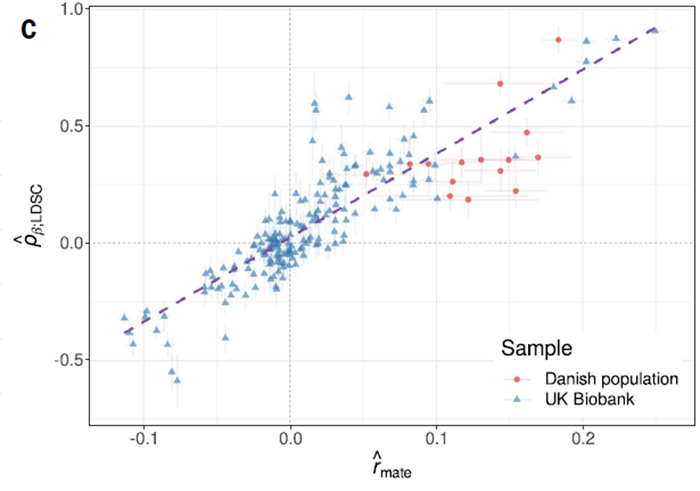
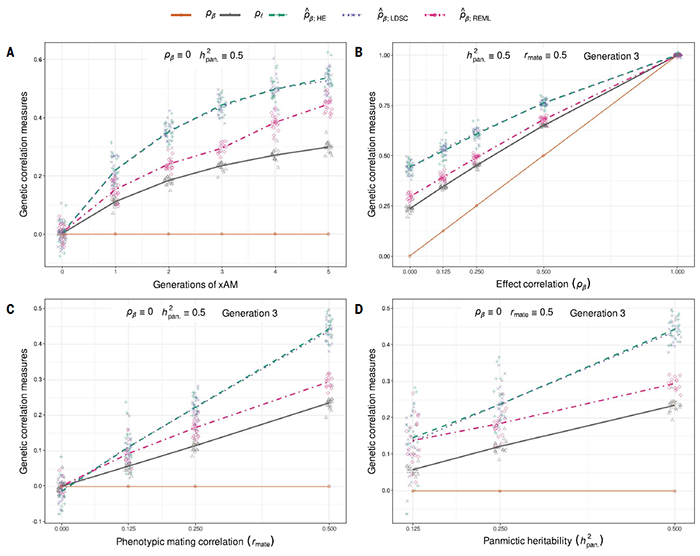
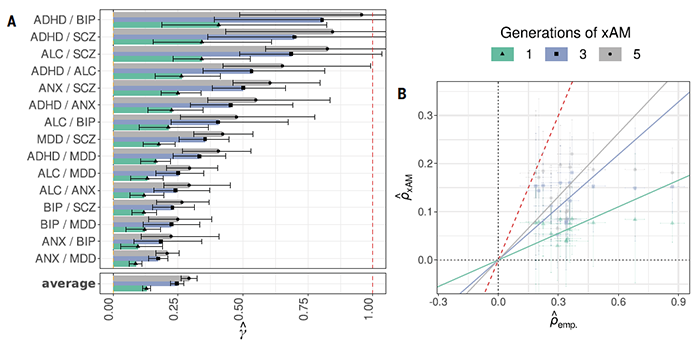
https://www.science.org/doi/10.1126/science.abo2059













